[本站讯] 近日,山东大学高等医学研究院王维教授团队在《自然-通讯》(Nature Communications)期刊在线发表题为“Trimbody with rigid AI-designed scaffolds enables atomic-resolution cryo-EM structure determination of small proteins”的研究论文。该研究设计出一种Trimbody通用性系统,实现了对小蛋白的原子分辨率冷冻电镜结构解析。山东大学王维教授、侯旭奔教授,自然资源部第三海洋研究所李增鹏教授为本文共同通讯作者。山东大学高等医学研究院博士生宋金扬、山东大学生物医学结构表征中心高级实验师齐磊为本文共同第一作者。
单颗粒冷冻电镜技术在大分子复合物结构解析中表现优异,但在小分子量蛋白(小于100 kDa)研究中长期受限于颗粒尺寸小、信噪比低和方向特征不足等问题,使其应用范围非常受限。为了突破这一瓶颈,研究人员普遍采用通过结合分子增加目标蛋白表现尺寸的策略,其中纳米抗体因其分子量小、稳定性高、易于重组表达和识别表位灵活等优势,成为理想的结合分子选择。
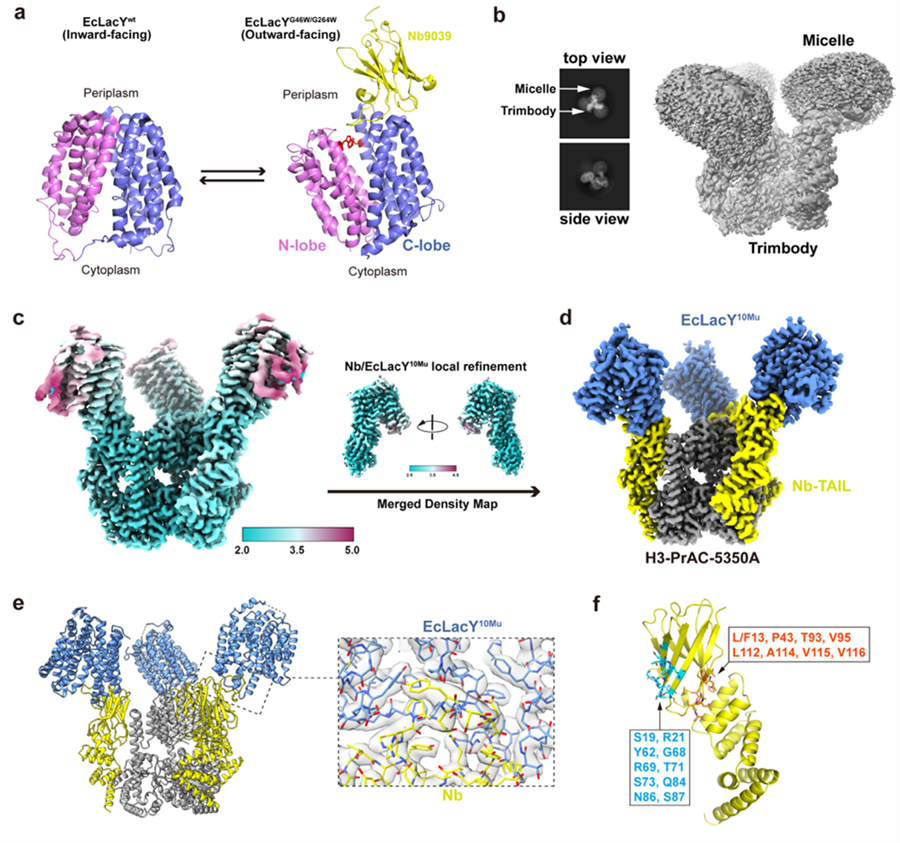
在本研究中,团队基于纳米抗体这一核心结合元件,通过RFdiffusion和ProteinMPNN等AI工具,从头设计出H3螺旋结构域与TAIL结构域,分别用于稳定纳米抗体与支架的结合并提升整体复合物的刚性,最终构建出由Nb-TAIL融合蛋白与H3-PrAC-5350A三聚体组成的Trimbody系统。该系统不仅结构简单、组装高效,而且通过引入AI设计的多重稳定界面,使纳米抗体与支架之间形成刚性连接,为靶蛋白冷冻电镜高分辨率解析创造了条件。
利用该系统,研究团队成功解析了四种分子量低于50 kDa的目标蛋白高分辨(3 Å以内)冷冻电镜结构,包括人源Gal10(2.62 Å)、Aequorea coerulescens来源GFP(2.29 Å)、人源Nectin4的IgV结构域(2.43 Å)以及膜蛋白大肠杆菌LacY(2.50 Å)。这些结构涵盖了可溶性与膜蛋白、不同结合模式的纳米抗体复合物,充分验证了Trimbody作为一个以纳米抗体为核心的普适性方法在多种小蛋白结构解析中的广泛适用性。Trimbody系统以其成本低廉、组装简单、与现有冷冻电镜工作流程的良好兼容性,为小分子量蛋白的高分辨率结构研究提供了新的通用工具,也为基于纳米抗体的药物研发及生命科学基础研究提供了重要支撑。该研究工作得到国家重点研发计划、国家自然科学基金、山东省自然科学基金等项目的资助。